COVID-19 é uma doença infecciosa causada pelo Coronavírus da Síndrome Respiratória Aguda Grave Tipo 2. Quando uma pessoa é infectada, os sintomas mais comuns incluem febre, tosse e falta de ar.
 As amostras usadas para teste podem ser coletadas por zaragatoas nasofaríngeas ou zaragatoas orofaríngeas.
As amostras usadas para teste podem ser coletadas por zaragatoas nasofaríngeas ou zaragatoas orofaríngeas.
O método padrão de detecção de coronavírus é a reação em cadeia da polimerase, PCR.Este é um método amplamente utilizado em biologia molecular.Ele pode copiar rapidamente de milhões a bilhões de fragmentos de DNA específicos.
 O novo coronavírus contém um genoma de RNA de cadeia simples muito longo.Para detectar esses vírus por PCR, as moléculas de RNA devem ser convertidas em suas sequências de DNA complementares pela transcriptase reversa e, em seguida, o DNA recém-sintetizado pode ser amplificado por procedimentos de PCR padrão, comumente conhecidos como RT-PCR.
O novo coronavírus contém um genoma de RNA de cadeia simples muito longo.Para detectar esses vírus por PCR, as moléculas de RNA devem ser convertidas em suas sequências de DNA complementares pela transcriptase reversa e, em seguida, o DNA recém-sintetizado pode ser amplificado por procedimentos de PCR padrão, comumente conhecidos como RT-PCR.
processo RT-PCR
extração de RNA
Para realizar este método, o RNA viral deve ser basicamente extraído.Uma variedade de kits de purificação de RNA pode ser usada para uma separação conveniente, rápida e eficaz.
Para extrair o RNA viral usando um kit comercial, primeiro adicione a amostra a um tubo de microcentrífuga e depois misture com o tampão de lise.Este tampão é altamente desnaturado e geralmente consiste em fenol e isotiocianato de guanidina.Além disso, os inibidores de RNase geralmente estão presentes no tampão de lise para garantir o isolamento do RNA viral intacto.
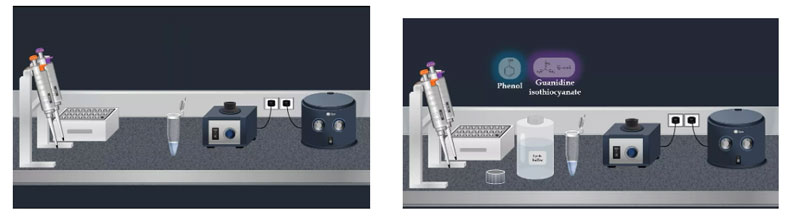 Depois de adicionar o tampão de lise, agitar o tubo de mistura por impulso e incubar à temperatura ambiente.O vírus é então lisado sob condições altamente desnaturantes fornecidas pelo tampão de lise.
Depois de adicionar o tampão de lise, agitar o tubo de mistura por impulso e incubar à temperatura ambiente.O vírus é então lisado sob condições altamente desnaturantes fornecidas pelo tampão de lise.
 Depois que a amostra é lisada, um tubo de centrífuga é usado para o procedimento de purificação.A amostra é carregada no tubo da centrífuga e então centrifugada.
Depois que a amostra é lisada, um tubo de centrífuga é usado para o procedimento de purificação.A amostra é carregada no tubo da centrífuga e então centrifugada.
 Este procedimento é um método de extração em fase sólida no qual a fase estacionária consiste em uma matriz de gel de sílica.
Este procedimento é um método de extração em fase sólida no qual a fase estacionária consiste em uma matriz de gel de sílica.
 Sob condições ideais de sal e pH, as moléculas de RNA se ligam à membrana de sílica.
Sob condições ideais de sal e pH, as moléculas de RNA se ligam à membrana de sílica.
 Ao mesmo tempo, proteínas e outros contaminantes são removidos.
Ao mesmo tempo, proteínas e outros contaminantes são removidos.
 Após a centrifugação, coloque o tubo da centrífuga em um tubo coletor limpo, descarte o filtrado e adicione o tampão de lavagem.
Após a centrifugação, coloque o tubo da centrífuga em um tubo coletor limpo, descarte o filtrado e adicione o tampão de lavagem.
 Coloque o tubo na centrífuga novamente para forçar o tampão de lavagem através da membrana.Isso removerá todas as impurezas restantes da membrana, deixando apenas o RNA ligado ao gel de sílica.
Coloque o tubo na centrífuga novamente para forçar o tampão de lavagem através da membrana.Isso removerá todas as impurezas restantes da membrana, deixando apenas o RNA ligado ao gel de sílica.
 Após a lavagem da amostra, coloque o tubo em um tubo de microcentrífuga limpo e adicione o tampão de eluição.
Após a lavagem da amostra, coloque o tubo em um tubo de microcentrífuga limpo e adicione o tampão de eluição.
 É então centrifugado para forçar o tampão de eluição através da membrana.O tampão de eluição remove o RNA viral da coluna giratória e obtém o RNA purificado livre de proteínas, inibidores e outros contaminantes.
É então centrifugado para forçar o tampão de eluição através da membrana.O tampão de eluição remove o RNA viral da coluna giratória e obtém o RNA purificado livre de proteínas, inibidores e outros contaminantes.
concentrado misto
Depois de extrair o RNA viral, o próximo passo é preparar a mistura de reação para amplificação por PCR.Nesta etapa, o concentrado é usado.Esta solução concentrada é uma solução concentrada pré-misturada que consiste em uma pré-mistura, transcriptase reversa, nucleotídeos, primer direto, primer reverso, sonda TaqMan e DNA polimerase.
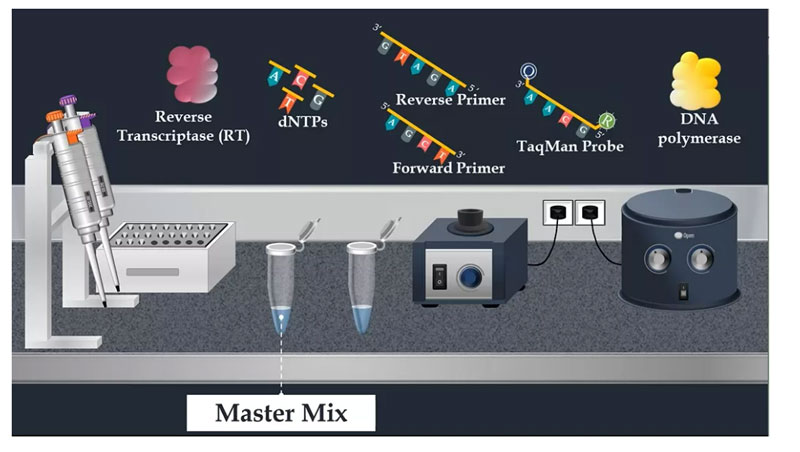 Finalmente, para completar esta mistura de reação, o molde de RNA é adicionado.Os tubos são misturados por vórtex de pulso e, em seguida, a mistura de reação é carregada na placa de PCR.A placa de PCR geralmente contém 96 poços e pode analisar várias amostras ao mesmo tempo.
Finalmente, para completar esta mistura de reação, o molde de RNA é adicionado.Os tubos são misturados por vórtex de pulso e, em seguida, a mistura de reação é carregada na placa de PCR.A placa de PCR geralmente contém 96 poços e pode analisar várias amostras ao mesmo tempo.
amplificação por PCR
Em seguida, coloque a placa na máquina de PCR, que é essencialmente um termociclador.
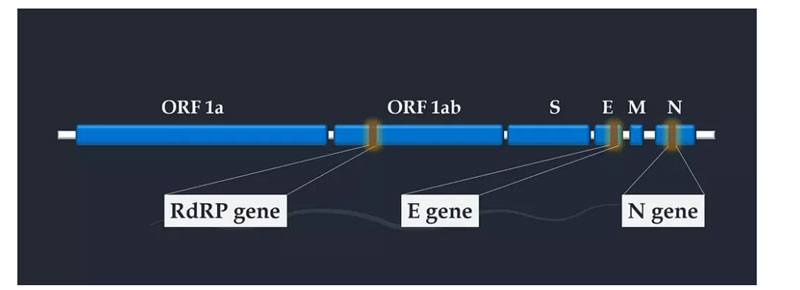
 O RT-PCR em tempo real é usado para detectar o novo coronavírus de 2019, amplificando a sequência alvo no gene RdrRP, gene E e gene N.A escolha do gene alvo depende do primer e da sequência da sonda.
O RT-PCR em tempo real é usado para detectar o novo coronavírus de 2019, amplificando a sequência alvo no gene RdrRP, gene E e gene N.A escolha do gene alvo depende do primer e da sequência da sonda.
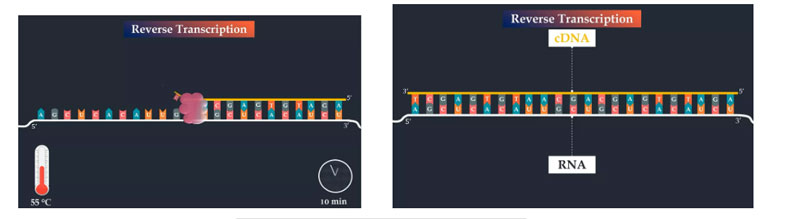
 A primeira etapa do RT-PCR é a transcrição reversa.É sintetizada a primeira fita de DNA complementar, que é iniciada pelo primer reverso da PCR, que se liga à parte complementar do genoma do RNA viral.Em seguida, a transcriptase reversa adiciona nucleotídeos de DNA à extremidade 3' do iniciador para sintetizar DNA complementar ao RNA viral.A temperatura e a duração desta etapa dependem dos primers, do RNA alvo e da transcriptase reversa usados.
A primeira etapa do RT-PCR é a transcrição reversa.É sintetizada a primeira fita de DNA complementar, que é iniciada pelo primer reverso da PCR, que se liga à parte complementar do genoma do RNA viral.Em seguida, a transcriptase reversa adiciona nucleotídeos de DNA à extremidade 3' do iniciador para sintetizar DNA complementar ao RNA viral.A temperatura e a duração desta etapa dependem dos primers, do RNA alvo e da transcriptase reversa usados.
 Em seguida, é aplicada uma etapa inicial de desnaturação, que resulta na desnaturação do híbrido RNA-DNA.Esta etapa é necessária para ativar a DNA polimerase.Ao mesmo tempo, a transcriptase reversa é inativada.
Em seguida, é aplicada uma etapa inicial de desnaturação, que resulta na desnaturação do híbrido RNA-DNA.Esta etapa é necessária para ativar a DNA polimerase.Ao mesmo tempo, a transcriptase reversa é inativada.
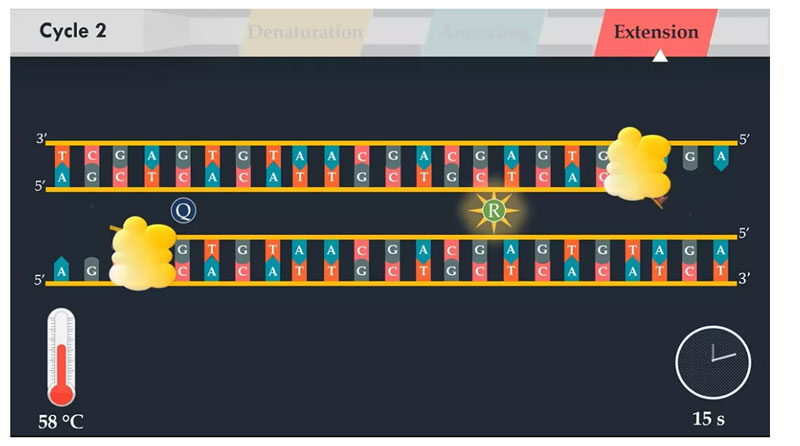
 A PCR consiste em uma série de ciclos térmicos.Cada ciclo consiste em etapas de desnaturação, recozimento e extensão.
A PCR consiste em uma série de ciclos térmicos.Cada ciclo consiste em etapas de desnaturação, recozimento e extensão.
 A etapa de desnaturação envolve aquecer a câmara de reação a 95 graus Celsius e usá-la para desnaturar o modelo de DNA de fita dupla.
A etapa de desnaturação envolve aquecer a câmara de reação a 95 graus Celsius e usá-la para desnaturar o modelo de DNA de fita dupla.
 Na próxima etapa, a temperatura da reação é reduzida para 58 graus Celsius, permitindo que o primer direto se una à parte complementar de seu modelo de DNA de fita simples.A temperatura de recozimento depende diretamente do comprimento e composição do primer.
Na próxima etapa, a temperatura da reação é reduzida para 58 graus Celsius, permitindo que o primer direto se una à parte complementar de seu modelo de DNA de fita simples.A temperatura de recozimento depende diretamente do comprimento e composição do primer.
 Na etapa de extensão, a DNA polimerase sintetiza uma nova fita de DNA que é complementar à fita molde de DNA.Adicionando núcleos livres complementares ao molde na direção 5' para 3' da mistura de reação.A temperatura desta etapa depende da DNA polimerase utilizada.
Na etapa de extensão, a DNA polimerase sintetiza uma nova fita de DNA que é complementar à fita molde de DNA.Adicionando núcleos livres complementares ao molde na direção 5' para 3' da mistura de reação.A temperatura desta etapa depende da DNA polimerase utilizada.
 Após o primeiro ciclo, um alvo de DNA de fita dupla é obtido.
Após o primeiro ciclo, um alvo de DNA de fita dupla é obtido.
 Em seguida, entre no segundo ciclo.O DNA de fita dupla é desnaturado para produzir duas moléculas de DNA de fita simples.
Em seguida, entre no segundo ciclo.O DNA de fita dupla é desnaturado para produzir duas moléculas de DNA de fita simples.
 Na próxima etapa, a temperatura da reação é reduzida, os primers são emparelhados com cada modelo de DNA de fita simples e a sonda Taq-man é combinada com a parte complementar do DNA alvo.
Na próxima etapa, a temperatura da reação é reduzida, os primers são emparelhados com cada modelo de DNA de fita simples e a sonda Taq-man é combinada com a parte complementar do DNA alvo.
 A sonda TaqMan consiste em um fluoróforo ligado covalentemente à extremidade 5' da sonda oligonucleotídica.Quando excitado pela fonte de luz do ciclador, o fluoróforo emite fluorescência.Além disso, a sonda é composta por um quencher na extremidade 3'.A proximidade do gene repórter ao extintor impede a detecção de fluorescência.
A sonda TaqMan consiste em um fluoróforo ligado covalentemente à extremidade 5' da sonda oligonucleotídica.Quando excitado pela fonte de luz do ciclador, o fluoróforo emite fluorescência.Além disso, a sonda é composta por um quencher na extremidade 3'.A proximidade do gene repórter ao extintor impede a detecção de fluorescência.
 Na etapa de extensão, a DNA polimerase sintetiza uma nova fita.Quando a polimerase atinge a sonda TaqMan, sua atividade 5'nuclease endógena cliva a sonda, separando o corante do extintor.
Na etapa de extensão, a DNA polimerase sintetiza uma nova fita.Quando a polimerase atinge a sonda TaqMan, sua atividade 5'nuclease endógena cliva a sonda, separando o corante do extintor.
 A cada ciclo de PCR, mais moléculas de corante são liberadas, resultando em um aumento na intensidade de fluorescência proporcional ao número de amplicons sintetizados.
A cada ciclo de PCR, mais moléculas de corante são liberadas, resultando em um aumento na intensidade de fluorescência proporcional ao número de amplicons sintetizados.
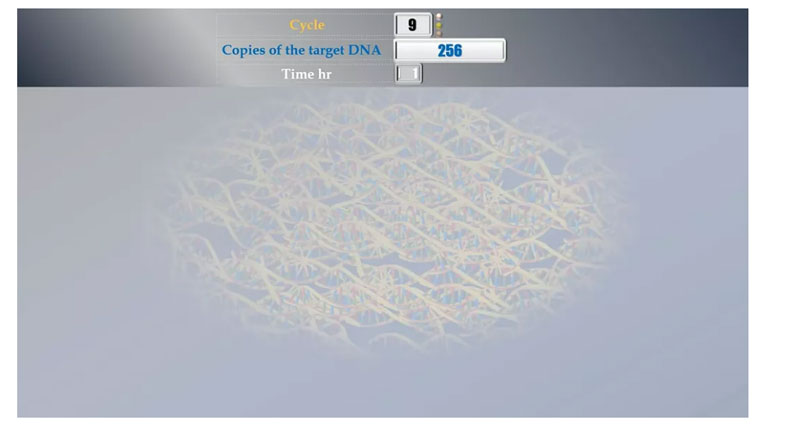
 Este método permite estimar o número de uma determinada sequência presente na amostra.O número de fragmentos de DNA de fita dupla dobra em cada ciclo.Portanto, a PCR pode ser usada para analisar amostras muito pequenas.
Este método permite estimar o número de uma determinada sequência presente na amostra.O número de fragmentos de DNA de fita dupla dobra em cada ciclo.Portanto, a PCR pode ser usada para analisar amostras muito pequenas.
 Para medir sinal fluorescente, lâmpada halógena de tungstênio, filtro de excitação, refletor, lente, filtro de emissão e câmera CCD de uso de dispositivo de carga acoplada.
Para medir sinal fluorescente, lâmpada halógena de tungstênio, filtro de excitação, refletor, lente, filtro de emissão e câmera CCD de uso de dispositivo de carga acoplada.
PASSO 4 Detectar
Para medir sinal fluorescente, lâmpada halógena de tungstênio, filtro de excitação, refletor, lente, filtro de emissão e câmera CCD de uso de dispositivo de carga acoplada.
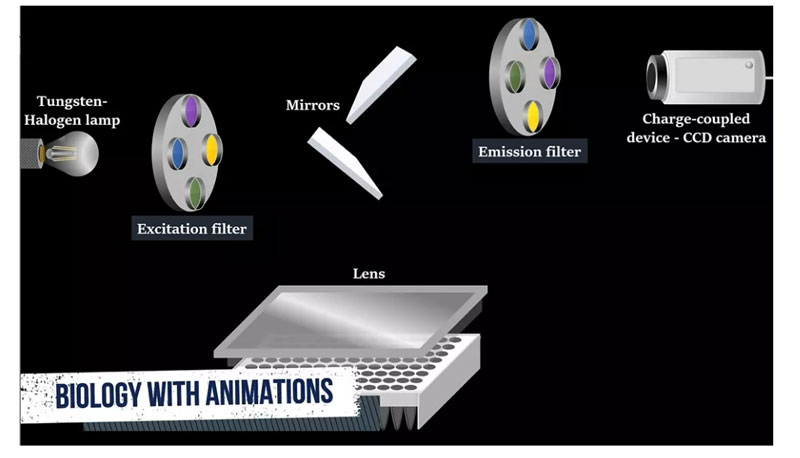 A luz filtrada da lâmpada é refletida pelo refletor, passa pela lente do condensador e é focada no centro de cada orifício.Em seguida, a fluorescência emitida pelo orifício é refletida no espelho, passa pelo filtro de emissão e é detectada pela câmera CCD.Em cada ciclo de PCR, a luz do fluoróforo autoexcitada pode ser detectada pelo CCD.
A luz filtrada da lâmpada é refletida pelo refletor, passa pela lente do condensador e é focada no centro de cada orifício.Em seguida, a fluorescência emitida pelo orifício é refletida no espelho, passa pelo filtro de emissão e é detectada pela câmera CCD.Em cada ciclo de PCR, a luz do fluoróforo autoexcitada pode ser detectada pelo CCD.
 Ele converte a luz capturada em dados digitais.Esse método é chamado de PCR em tempo real e permite o monitoramento em tempo real do progresso da reação de PCR.
Ele converte a luz capturada em dados digitais.Esse método é chamado de PCR em tempo real e permite o monitoramento em tempo real do progresso da reação de PCR.
Horário da postagem: 19 de julho de 2021













