Nos últimos dez anos, a tecnologia de edição de genes baseada em CRISPR desenvolveu-se rapidamente e foi aplicada com sucesso ao tratamento de doenças genéticas e câncer em ensaios clínicos em humanos.Ao mesmo tempo, cientistas de todo o mundo estão constantemente explorando novas ferramentas com potencial de edição de genes para resolver os problemas das ferramentas e decisões de edição de genes existentes.
Em setembro de 2021, a equipe de Zhang Feng publicou um artigo na revista Science [1] e descobriu que uma ampla gama de transposters codificava enzimas de ácido nucleico guiadas por RNA e o nomeou sistema Omega (incluindo ISCB, ISRB, TNP8).O estudo também descobriu que o sistema Omega usa uma seção de RNA para guiar a cadeia dupla de DNA de corte, ou seja, ωRNA.Mais importante, essas enzimas de ácido nucleico são muito pequenas, apenas cerca de 30% de CAS9, o que significa que é mais provável que sejam entregues às células.

Em 12 de outubro de 2022, a equipe de Zhang Feng publicou na revista Nature intitulado: Estrutura do Omega Nickase ISRB em complexo com ωrna e DNA alvo [2].
O estudo analisou ainda mais a estrutura do microscópio eletrônico congelado do ISRB-ωRNA e o complexo de DNA alvo no sistema Omega.
O ISCB é o ancestral do CAS9 e o ISRB é o mesmo objeto da falta do domínio de ácido nucleico HNH do ISCB, portanto, o tamanho é menor, apenas cerca de 350 aminoácidos.O DNA também fornece a base para um maior desenvolvimento e transformação de engenharia.

O IsrB guiado por RNA é um membro da família OMEGA codificada pela superfamília de transposons IS200/IS605.A partir da análise filogenética e dos domínios únicos compartilhados, é provável que IsrB seja o precursor de IscB, que é o ancestral de Cas9.
Em maio de 2022, o Lovely Dragon Laboratory da Cornell University publicou um artigo na revista Science [3], analisando a estrutura do IscB-ωRNA e seu mecanismo de corte do DNA.

Comparado com IscB e Cas9, IsrB não possui o domínio HNH nuclease, o lóbulo REC e a maioria dos domínios de interação de sequência PAM, então IsrB é muito menor que Cas9 (apenas cerca de 350 aminoácidos).No entanto, o tamanho pequeno de IsrB é equilibrado por um RNA guia relativamente grande (seu RNA ômega tem cerca de 300 nt de comprimento).
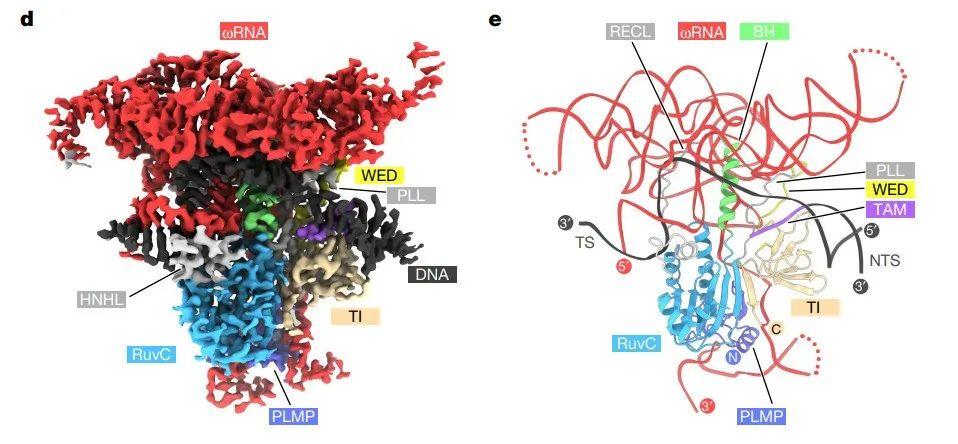
A equipe de Zhang Feng analisou a estrutura do microscópio crioeletrônico de IsrB (DtIsrB) da bactéria anaeróbia de calor úmido Desulfovirgula thermocuniculi e seu complexo de ωRNA e DNA alvo.A análise estrutural mostrou que a estrutura geral da proteína IsrB compartilhava uma estrutura principal com a proteína Cas9.
Mas a diferença é que Cas9 usa o lóbulo REC para facilitar o reconhecimento do alvo, enquanto IsrB depende de seu ωRNA, parte do qual forma uma estrutura tridimensional complexa que age como REC.
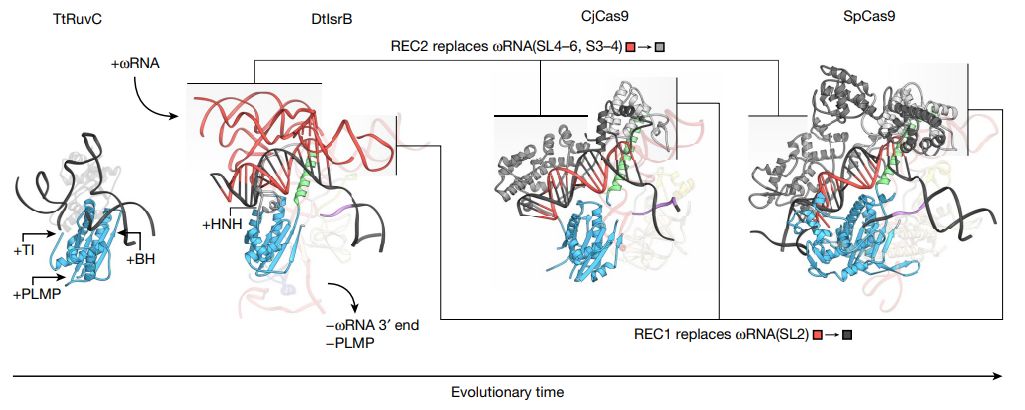
Para entender melhor as mudanças estruturais de IsrB e Cas9 durante a evolução de RuvC, a equipe de Zhang Feng comparou as estruturas alvo de ligação ao DNA de RuvC (TtRuvC), IsrB, CjCas9 e SpCas9 de Thermus thermophilus.
A análise estrutural de IsrB e seu ωRNA esclarece como IsrB-ωRNA reconhece e cliva conjuntamente o DNA alvo e também fornece uma base para desenvolvimento e engenharia adicionais dessa nuclease miniaturizada.Comparações com outros sistemas guiados por RNA destacam interações funcionais entre proteínas e RNAs, avançando nossa compreensão da biologia e evolução desses diversos sistemas.
Links:
1.https://www.science.org/doi/10.1126/science.abj6856
2.https://www.science.org/doi/10.1126/science.abq7220
3. https://www.nature.com/articles/s41586-022-05324-6
Horário da postagem: 14 de outubro de 2022








